| Disponibilidade: | |
|---|---|
| Quantidade: | |











Amplo portfólio de modelos – Abrange SRC eosinofílica (papaína), SRC induzida por protease fúngica (Aspergillus), SRC associada a superantígenos (SEB) e rinite alérgica clássica (OVA).
Múltiplas cepas – C57BL/6 e BALB/c disponíveis para atender diferentes origens genéticas e vieses Th1/Th2.
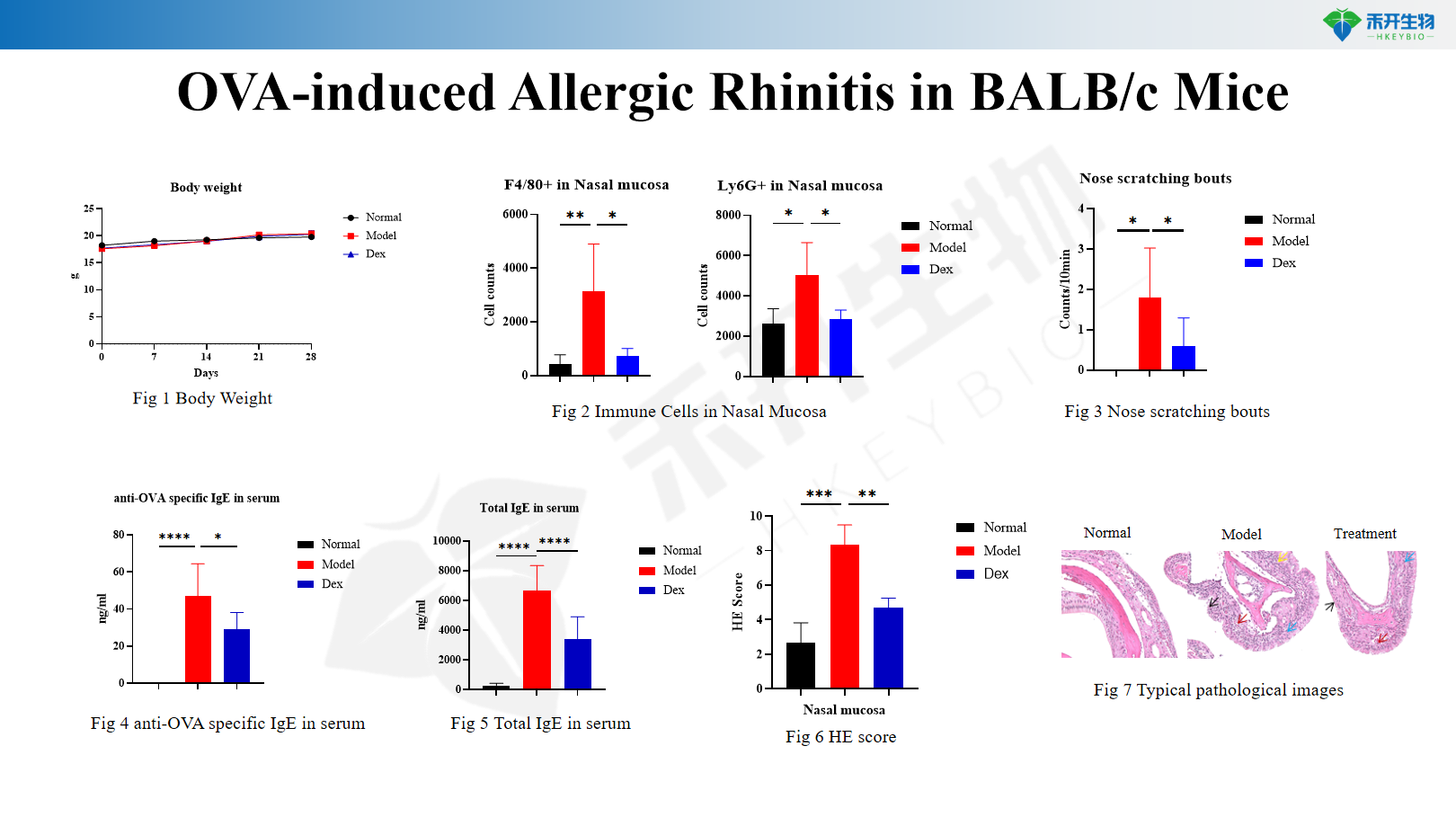
Endpoints abrangentes – Peso corporal, contagem de células de lavagem nasal (eosinófilos, células totais), IgE sérica (total e específica de OVA), comportamento de coçar nasal, histopatologia da mucosa nasal (HE), perfil de citocinas (IL-33, citocinas Th2).
Valor translacional – Ideal para testar corticosteróides, anti-histamínicos, produtos biológicos (anti-IgE, anti-IL-5, anti-IL-4Rα) e novos imunomoduladores.
Pacotes de dados prontos para IND – Os estudos podem ser conduzidos de acordo com os princípios das BPL.
Modelo de rinossinusite eosinofílica C57BL/6 induzida por papaína
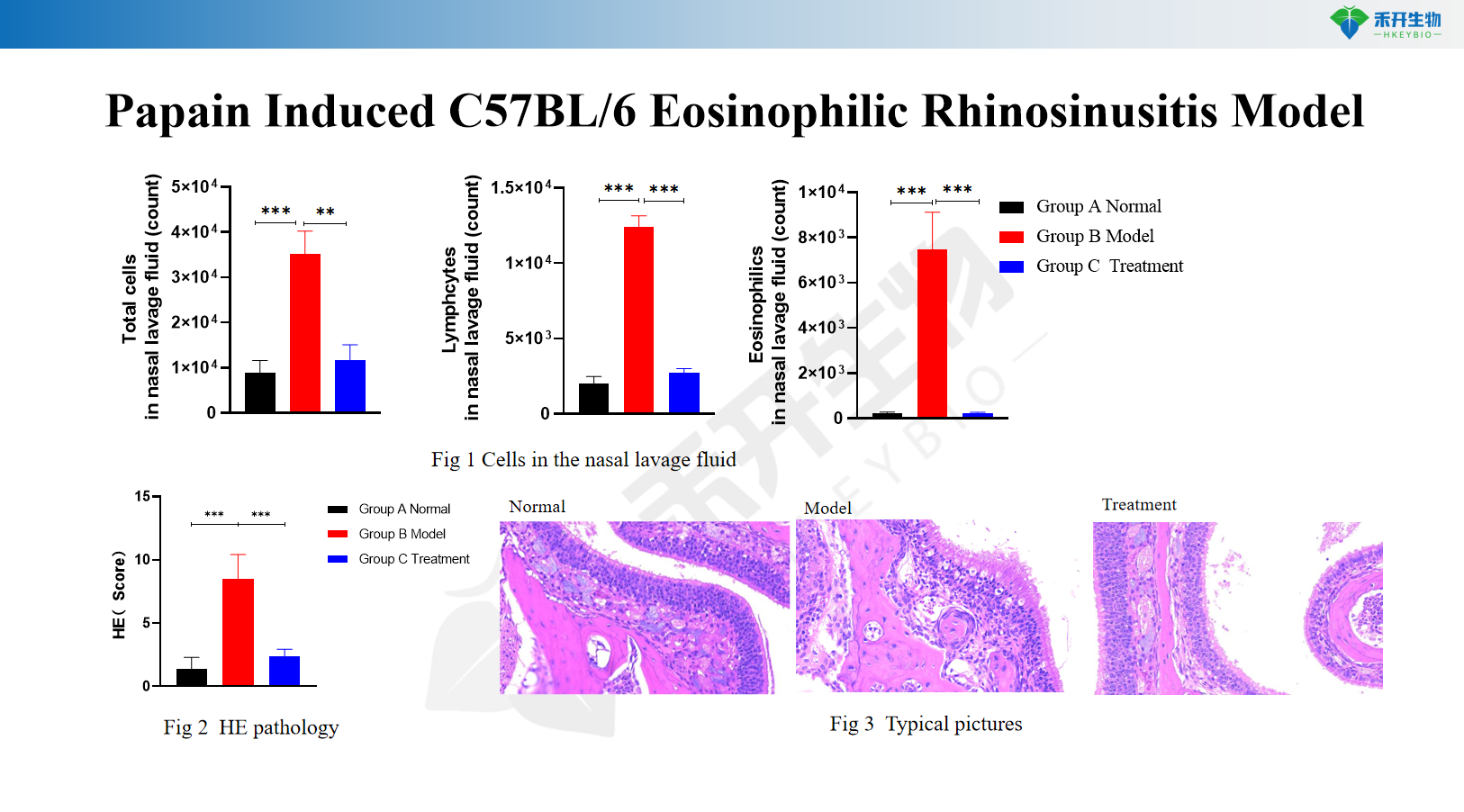
Proteinase de Aspergillus oryzae e modelo CRS C57BL/6 induzido por OVA
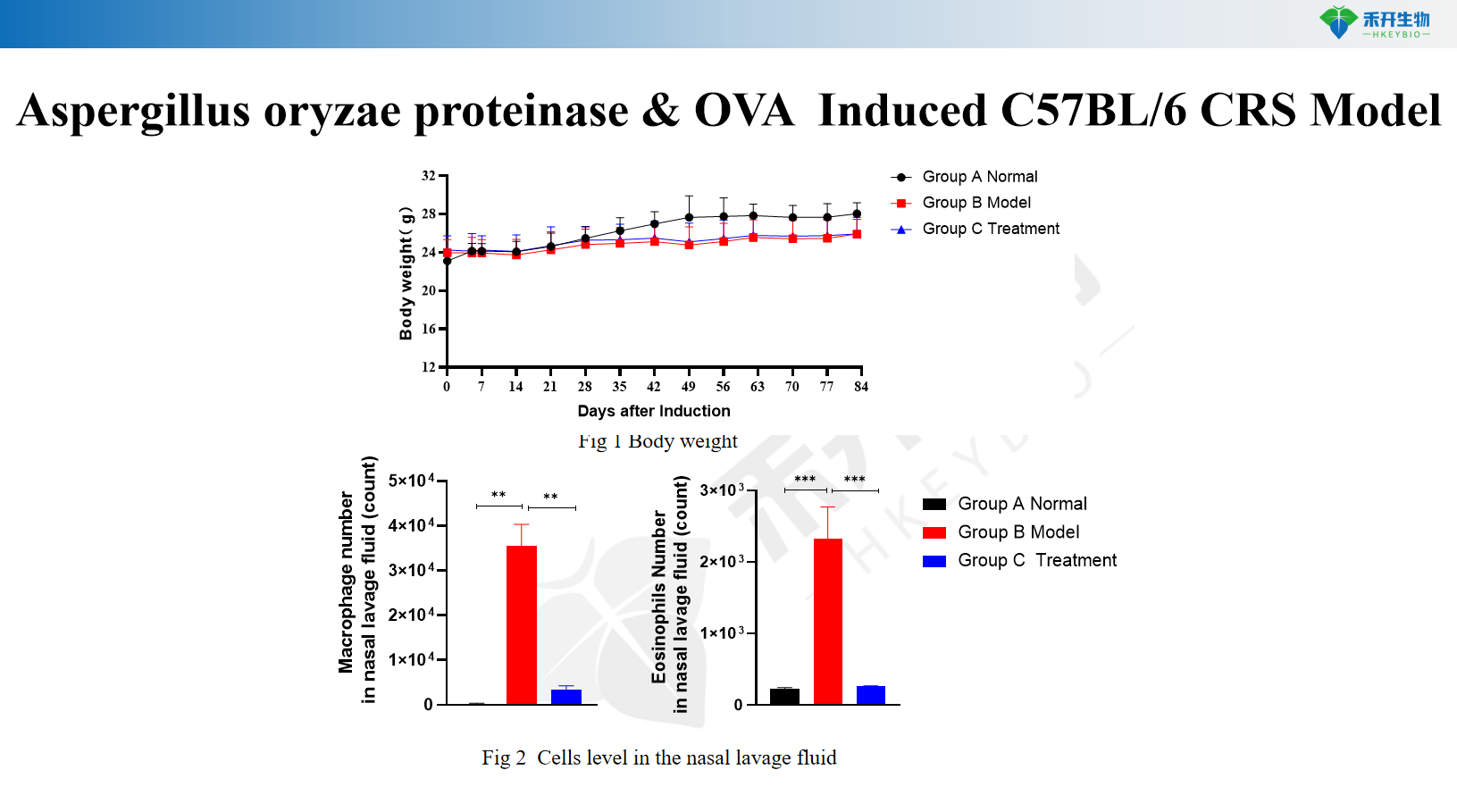
Proteinase de Aspergillus oryzae e modelo BALB/c CRS induzido por OVA
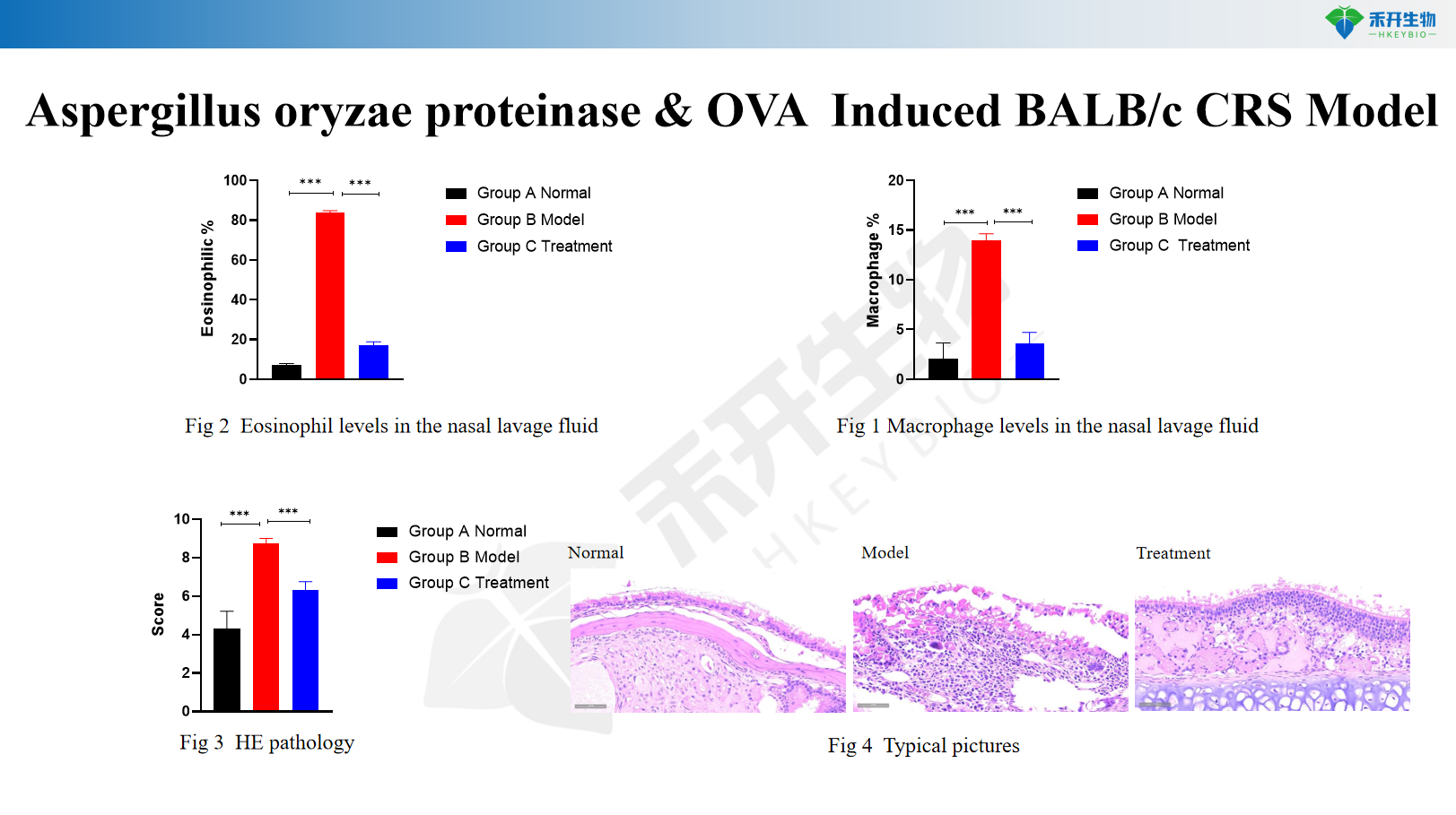
Modelo CRS induzido por SEB e OVA
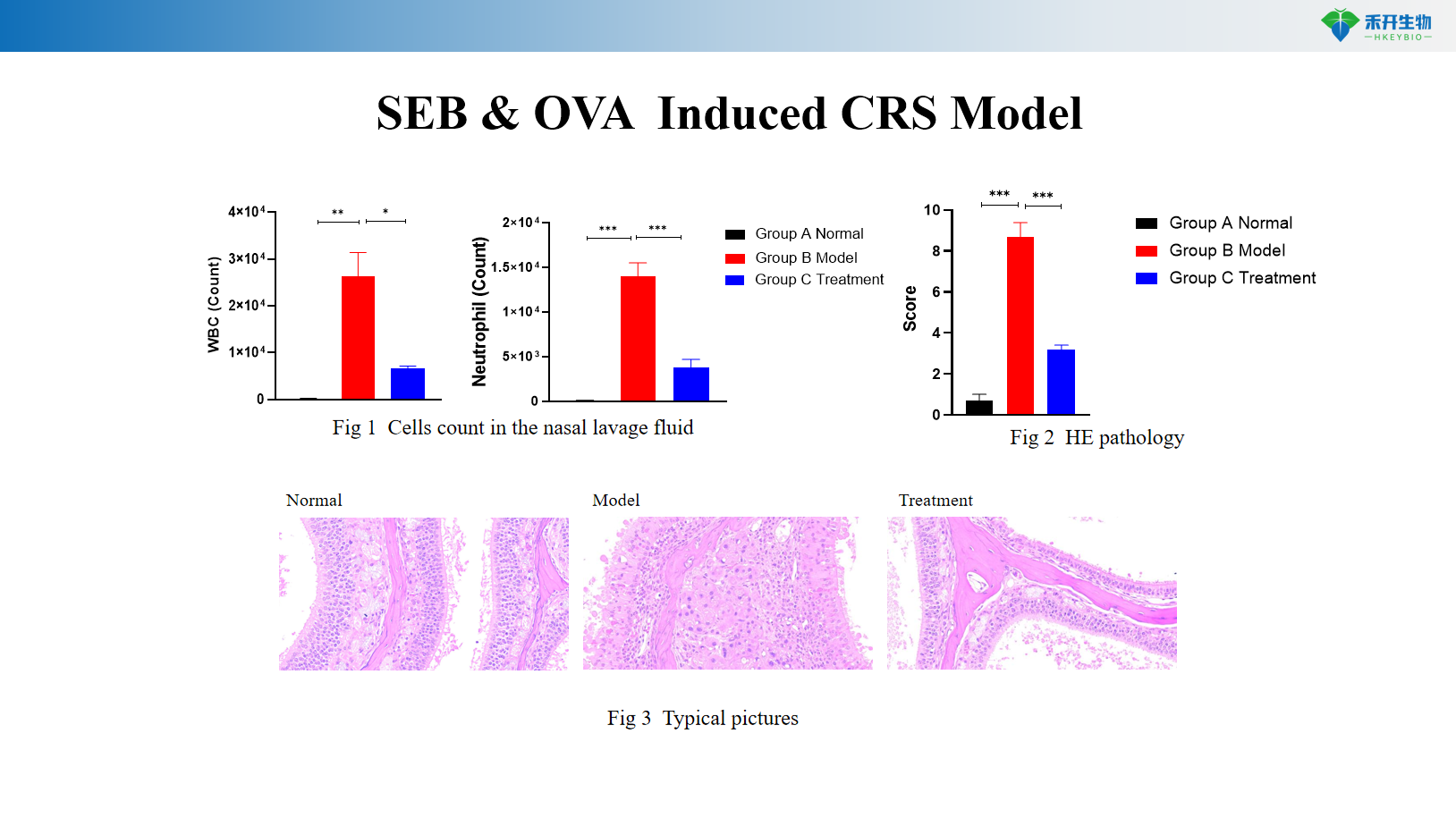
Rinite Alérgica Induzida por OVA em Camundongos BALB/c
• Teste de eficácia de corticosteroides intranasais e sistêmicos, anti-histamínicos e descongestionantes
• Avaliação de produtos biológicos direcionados às vias Th2 (anti-IL-4Rα, anti-IL-5, anti-IL-13, anti-IgE)
• Validação de alvo para citocinas derivadas de epitélio (TSLP, IL-33, IL-25) e vias ativadas por protease
• Descoberta de biomarcadores (IgE, peroxidase de eosinófilos, assinaturas de citocinas)
• Estudos de farmacologia e toxicologia que permitem IND
Parâmetro |
Especificação |
Espécie/Estirpe |
Rato (C57BL/6, BALB/c) |
Método de indução |
Papaína (protease); protease de Aspergillus + OVA; SEB + ÓVULOS; OVA + alume |
Duração do estudo |
3–6 semanas (fases de sensibilização + desafio) |
Principais pontos de extremidade |
Peso corporal, contagem de células da lavagem nasal (total e diferencial), IgE sérica total e IgE específica para OVA, comportamento de coçar nasal (rinite alérgica), histopatologia da mucosa nasal (pontuação HE para inflamação, infiltração eosinofílica, hiperplasia de células caliciformes), níveis de citocinas (IL-4, IL-5, IL-13, IL-33) no tecido/lavagem nasal |
Pacote de dados |
Dados brutos, relatórios de análise, citologia de lavagem nasal, resultados de ELISA, lâminas histológicas, dados comportamentais, bioinformática (opcional) |
P: Como escolho o modelo certo para o meu medicamento candidato?
R: Para RSC eosinofílica, são recomendados modelos de papaína ou Aspergillus protease. Para SRC associada a superantígenos, o modelo SEB+OVA é apropriado. Para a rinite alérgica clássica, o modelo OVA é a escolha padrão. Camundongos BALB/c exibem respostas Th2 mais fortes, enquanto C57BL/6 permitem o uso de linhagens transgênicas. Nossa equipe científica pode orientar a seleção do modelo com base no seu alvo específico.
P: Qual é o papel da atividade da protease nos modelos CRS?
R: As proteases (papaína, protease de Aspergillus) rompem as junções estreitas epiteliais, levando à disfunção da barreira e à liberação de citocinas epiteliais (IL-33, TSLP), que impulsionam a inflamação tipo 2 e a infiltração eosinofílica, mimetizando a fisiopatologia da SRC humana.
P: Esses modelos podem ser usados para estudos que permitem o IND?
R: Sim. Os estudos podem ser conduzidos de acordo com os princípios das BPL para submissões regulatórias (FDA, EMA).
P: Vocês oferecem protocolos de estudo personalizados (por exemplo, diferentes doses de alérgenos, cronogramas de sensibilização)?
R: Absolutamente. Nossa equipe científica adapta protocolos de indução, cronogramas de tratamento e análises de desfechos para seu medicamento candidato específico.
