| Disponibilità: | |
|---|---|
| Quantità: | |











Ampio portafoglio di modelli : copre la CRS eosinofila (papaina), la CRS indotta da proteasi fungina (Aspergillus), la CRS associata a superantigeni (SEB) e la rinite allergica classica (OVA).
Ceppi multipli : C57BL/6 e BALB/c disponibili per adattarsi a diversi background genetici e bias Th1/Th2.
Endpoint completi : peso corporeo, conta delle cellule del lavaggio nasale (eosinofili, cellule totali), IgE sieriche (totali e specifiche per OVA), comportamento di grattamento nasale, istopatologia della mucosa nasale (HE), profilazione delle citochine (IL-33, citochine Th2).
Valore traslazionale – Ideale per testare corticosteroidi, antistaminici, farmaci biologici (anti-IgE, anti-IL-5, anti-IL-4Rα) e nuovi immunomodulatori.
Pacchetti dati pronti per IND – Gli studi possono essere condotti in conformità con i principi GLP.
Modello di rinosinusite eosinofila indotta da papaina C57BL/6
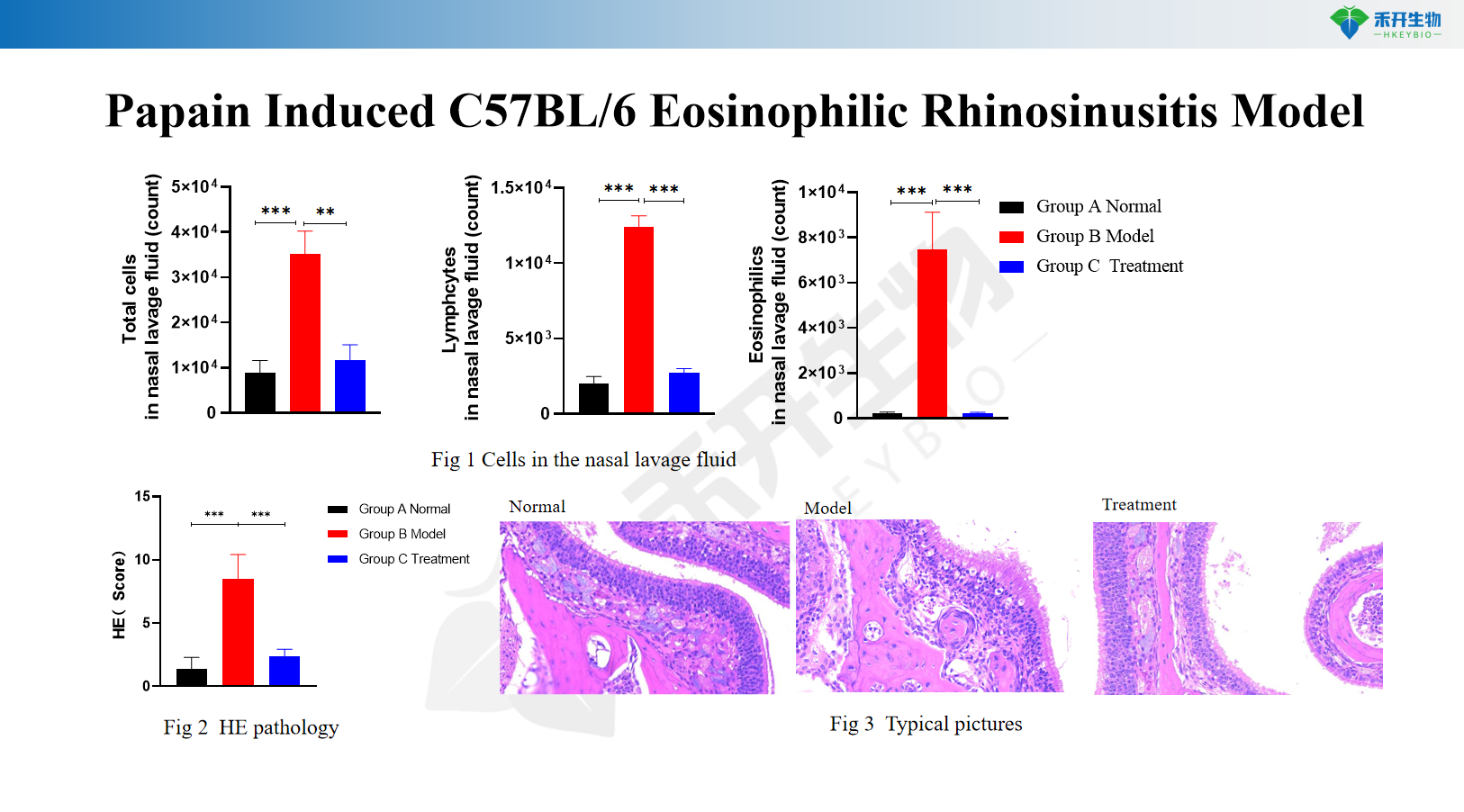
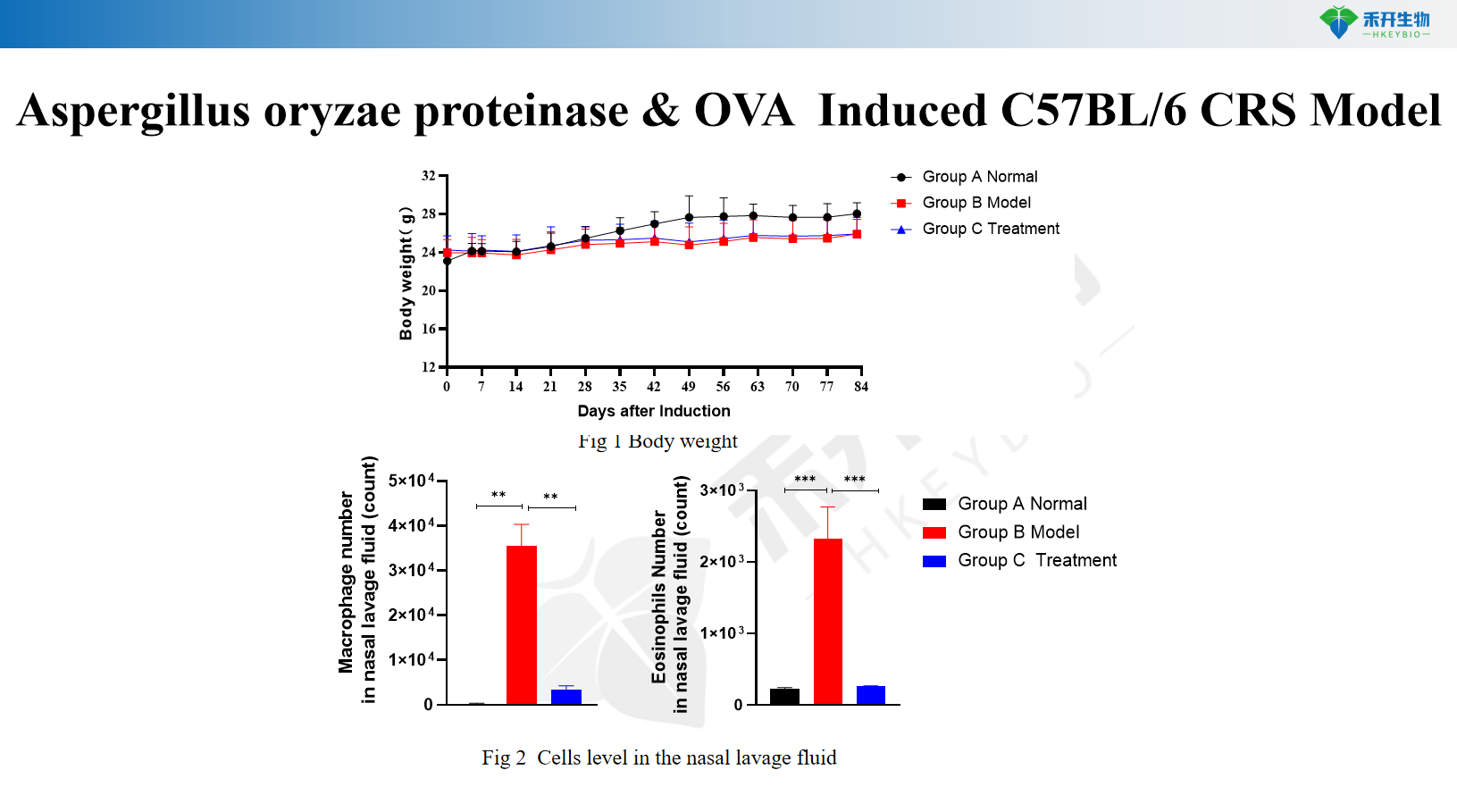
Modello CRS C57BL/6 indotto da proteinasi di Aspergillus oryzae e OVA
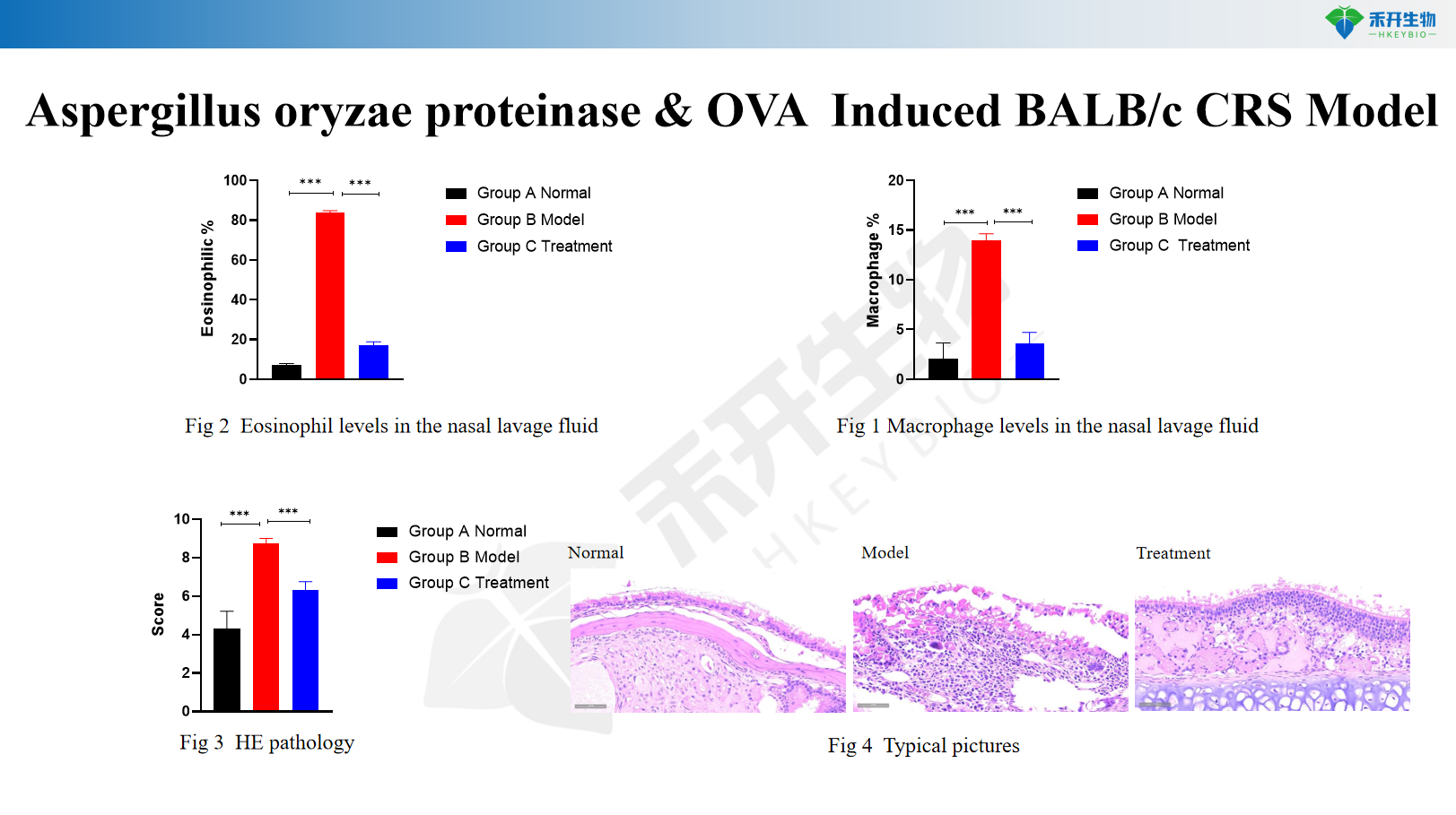
Modello CRS BALB/c indotto da proteinasi di Aspergillus oryzae e OVA
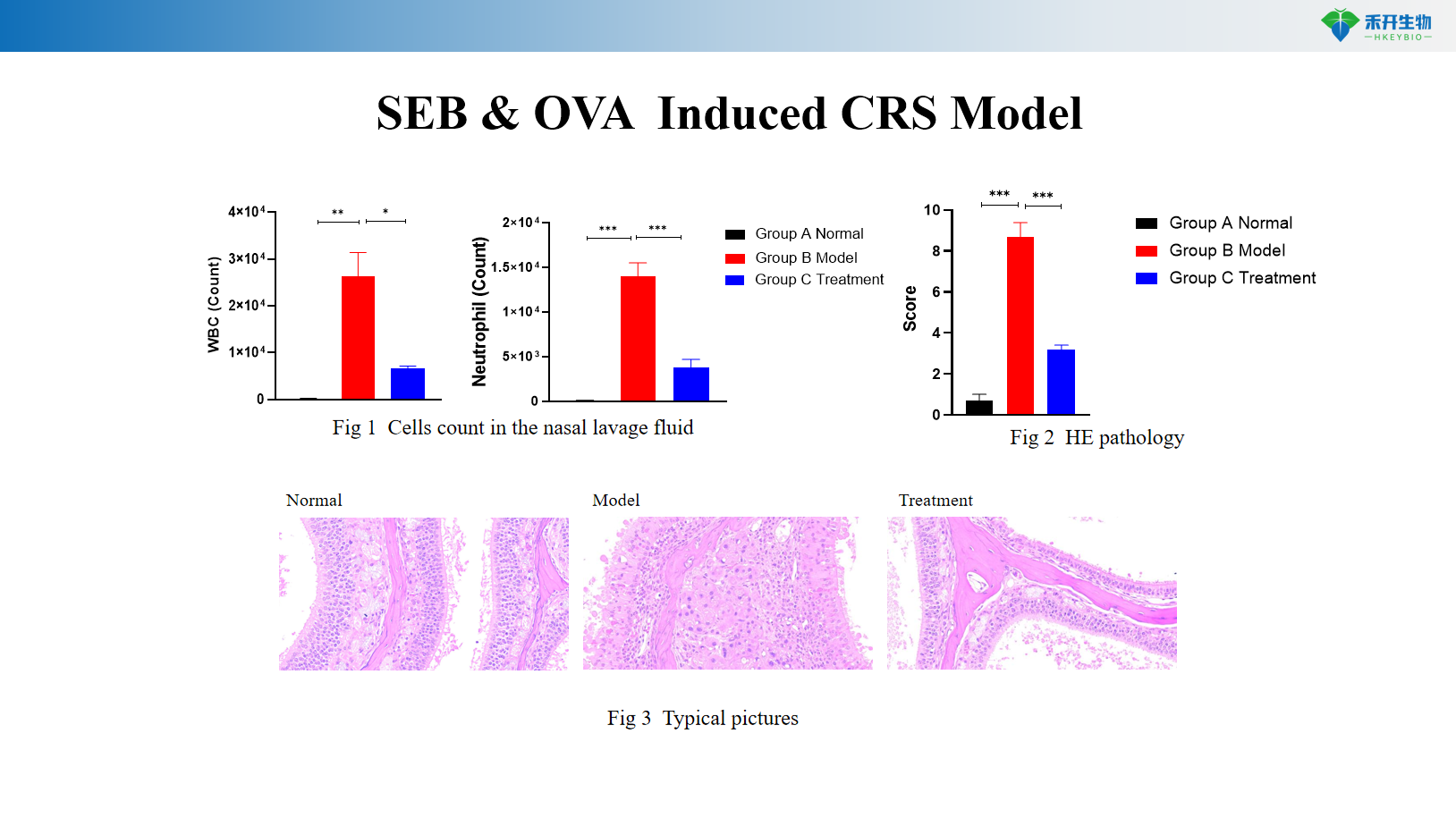
Modello CRS indotto da SEB e OVA
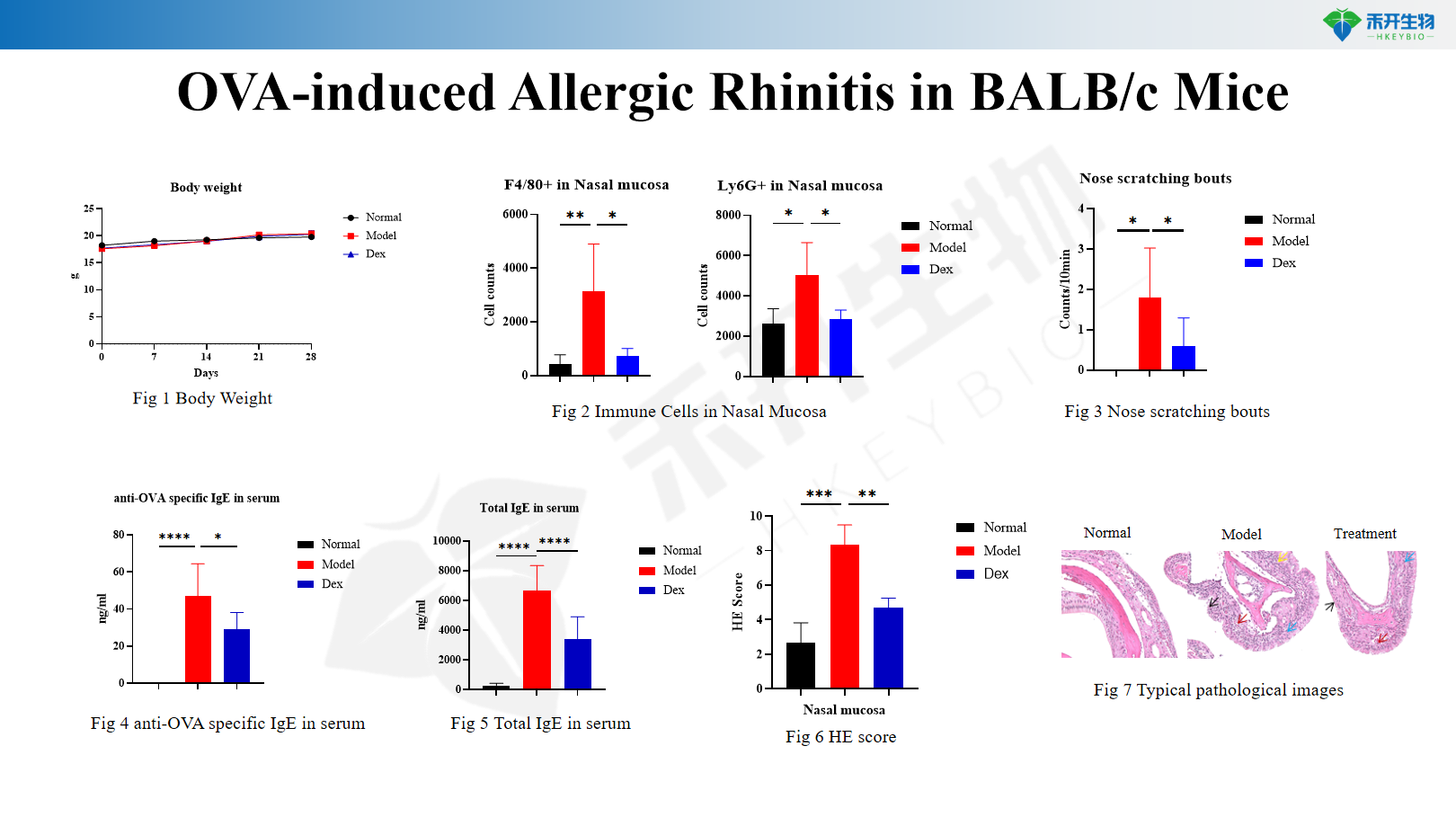
Rinite allergica indotta da OVA nei topi BALB/c
• Test di efficacia di corticosteroidi intranasali e sistemici, antistaminici e decongestionanti
• Valutazione di farmaci biologici mirati alle vie Th2 (anti-IL-4Rα, anti-IL-5, anti-IL-13, anti-IgE)
• Convalida del target per citochine di derivazione epiteliale (TSLP, IL-33, IL-25) e percorsi attivati dalla proteasi
• Scoperta di biomarcatori (IgE, perossidasi eosinofila, firme di citochine)
• Studi farmacologici e tossicologici che consentono l'IND
Parametro |
Specifica |
Specie/ceppo |
Topo (C57BL/6, BALB/c) |
Metodo di induzione |
Papaina (proteasi); Proteasi dell'Aspergillus + OVA; SEB+OVA; OVA + allume |
Durata dello studio |
3–6 settimane (fasi di sensibilizzazione + sfida) |
Endpoint chiave |
Peso corporeo, conta delle cellule del lavaggio nasale (totale e differenziale), IgE totali nel siero e IgE specifiche per OVA, comportamento di grattamento nasale (rinite allergica), istopatologia della mucosa nasale (punteggio HE per infiammazione, infiltrazione eosinofila, iperplasia delle cellule caliciformi), livelli di citochine (IL-4, IL-5, IL-13, IL-33) nel tessuto/lavaggio nasale |
Pacchetto dati |
Dati grezzi, rapporti di analisi, citologia del lavaggio nasale, risultati ELISA, vetrini istologici, dati comportamentali, bioinformatica (facoltativo) |
D: Come scelgo il modello giusto per il mio farmaco candidato?
R: Per la CRS eosinofila, si consigliano modelli con papaina o proteasi di Aspergillus. Per la CRS associata al superantigene, il modello SEB+OVA è appropriato. Per la rinite allergica classica, il modello OVA è la scelta standard. I topi BALB/c mostrano risposte Th2 più forti, mentre C57BL/6 consentono l'uso di linee transgeniche. Il nostro team scientifico può guidare la selezione del modello in base al tuo target specifico.
D: Qual è il ruolo dell'attività della proteasi nei modelli CRS?
R: Le proteasi (papaina, proteasi dell'Aspergillus) interrompono le giunzioni strette epiteliali, portando alla disfunzione della barriera e al rilascio di citochine epiteliali (IL-33, TSLP), che guidano l'infiammazione di tipo 2 e l'infiltrazione eosinofila, imitando la fisiopatologia della CRS umana.
D: Questi modelli possono essere utilizzati per studi abilitanti all’IND?
R: Sì. Gli studi possono essere condotti in conformità con i principi GLP per le richieste normative (FDA, EMA).
D: Offrite protocolli di studio personalizzati (ad esempio, diverse dosi di allergeni, programmi di sensibilizzazione)?
R: Assolutamente. Il nostro team scientifico adatta protocolli di induzione, programmi di trattamento e analisi degli endpoint al tuo specifico farmaco candidato.
